
通过福尔马林固定石蜡包埋FFPE(Formalin-fixed paraffin-embedded)保存样品已经使用了一个多世纪,然而将染色质分析技术应用于FFPE样品进展有限。虽然对于FFPE样品已经开发了染色质免疫沉淀测序(ChIP-seq)等方法,但是ChIP-seq不适用于从患者样本中获得的少量起始材料。
2023年9月研究者Steven Henikoff在Nature Communications期刊(16.6/Q1)上发表了文章“Epigenomic analysis of formalin-fixed paraffin-embedded samples by CUT&Tag”。作者介绍了靶向染色质可及性切割 (CUTAC),这是一种基于 CUT&Tag 的抗体靶向染色质可及性作图方案。作者发现 FFPE-CUTAC 产生的转录调控元件差异可区分小鼠脑肿瘤,并以高置信度和精确度识别和绘制调控元件标记,包括 RNA-seq 无法检测到的 microRNA。该项研究对存档的生物样本进行表观基因组分析成为可能。
实验设计
样本类型:荷瘤小鼠和正常小鼠的大脑组织制作的FFPE(n=10);健康小鼠肝脏和肝内胆管癌小鼠肝脏制作的FFPE(n=5),保存时间从1个月到2年不等。
测序策略:Illumina NextSeq 2000,PE250
主要结果
一、CUT&Tag简化了全细胞的方案

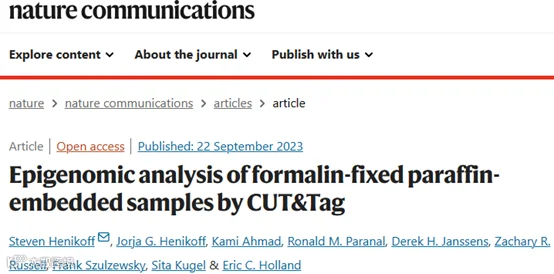
作者引入了CUT&Tag技术,后来简化了这个方案,可以在单个PCR管中完成,使用58°C孵育,加入0.1% SDS,然后加入过量的Triton-X100,将SDS封装在胶束中,从而实现高效的PCR。然而,这种CUT&Tag-direct方法只适用于最多约50,000个细胞核,因为发现更多的材料会抑制PCR。当应用于H3K4me3启动子标记时,这种修改后的CUT&Tag-direct方案适用于原生整个细胞,得到了与原生或固定核使用原始有机提取方法或CUT&Tag-direct相匹配的代表性图谱。基于MACS2峰值调用和峰值内读取的分数(FRiP),我们使用修改后的方案对至少100,000个原生整个细胞进行了略微更多的峰值调用,并获得了类似的FRiP值。
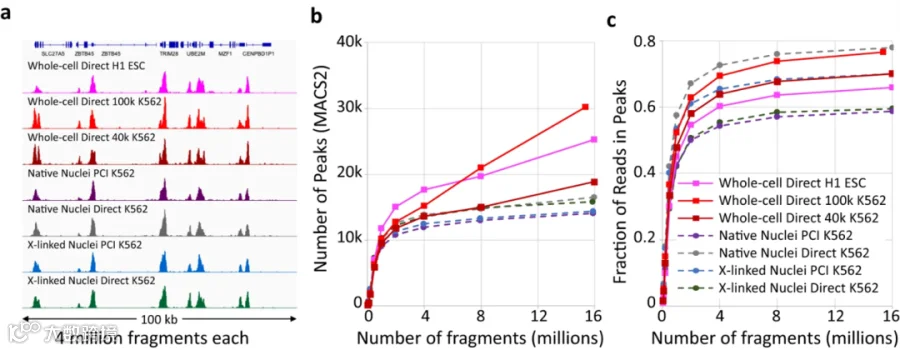
图1. 全细胞的CUT&Tag带来的高数据质量
二、CUTAC中FFPE切片的温度依赖性渗透化
作者选择了三种不同机制驱动的相关小鼠中枢神经系统肿瘤类型的石蜡块,来评估区分样本的能力。比较了由酪氨酸激酶活化的PDGFB驱动的胶质瘤、ZFTA-RELA基因融合驱动的室管膜瘤和YAP1FAM118b基因融合驱动的室管膜瘤的FFPE块中的10微米切片,以及与正常小鼠脑的FFPE块之间的差异。在FFPE上执行CUT&Tag-direct的难度不仅因为重度福尔马林固定引起的严重染色质损伤,还因为细胞嵌入其中的大量交联的细胞内和细胞间物质。甲醛交联可通过在升高的温度下孵育来逆转。典型的ChIP-seq、CUT&RUN和CUT&Tag方案建议在65°C的条件下过夜孵育,同时加入蛋白酶K和SDS以同时逆转交联和脱蛋白化。然而,用于制备FFPE的更极端的甲醛处理需要高达90°C的孵育温度,以分离用于全基因组测序的PCR可扩增的DNA。为了优化从小鼠脑肿瘤的FFPE样本中进行DNA恢复和抗原表位检索的孵育温度,作者在ConA珠子和抗体添加之前,在65°C到95°C的温度范围内孵育了剪切的FFPE样本。在DNA测序后,映射到小鼠基因组的片段比例表现出了很强的温度依赖性,其中最高温度(90-95°C)显示出了映射到小鼠基因组的最高比例(75%),而最低温度(65-70°C)显示出了最低比例(13%)。作者确定了甲醛交联逆转与孵育温度之间存在一定关系。
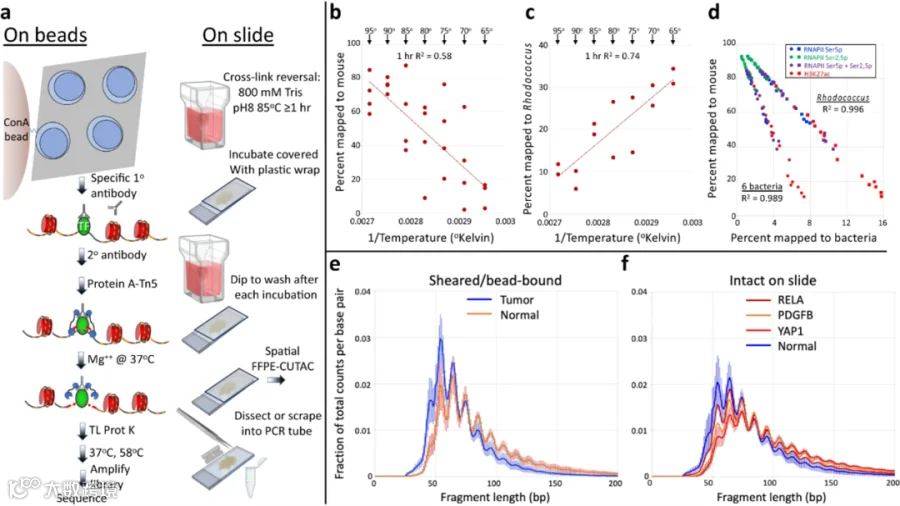
图2.高温可提高FFPE-CUTAC的小鼠片段得率
三、高温有助于优先减少杂质细菌DNA的标记化
通过对Genbank中的核苷酸序列进行BLASTN分析,作者发现对于所有样本,革兰氏阳性细菌红球菌(Rhodococcus erythropolis)始终排在列表的前列。将片段映射到基因组,发现整个基因组都如预期地表示出来,这表明这种物种可能是研究中小鼠脑FFPE的主要污染物。并且发现片段映射到小鼠和映射到R. erythropolis基因组的比例之间存在接近完美的反相关关系,这可能解释了随着温度升高,Rhodococcus污染减少的原因。
1.直接在玻片上进行的FFPE-CUTAC
高温和严格的洗涤不能完全消除细菌污染,但作者怀疑珠子上的Concanavalin A可能捕获了残留的死细菌细胞。作者用氨基包被的顺磁珠替代了ConA珠子,还测试了热水去脂化,最后作者测试了一种无珠子的方法,即在85°C下过夜孵育,然后在用塑料薄膜覆盖的玻片上进行孵育和浸泡洗涤。观察到使用没有ConA的磁性珠子或直接在玻片上进行FFPE-CUTAC都导致99%的映射性能,完全消除了残留的细菌污染。
2.FFPE-CUTAC生成高质量的活性染色质图谱
为了评估应用于小鼠脑肿瘤的FFPE-CUTAC的准确性和数据质量,作者比较了使用相同的H3K27ac抗体从相同研究中获得的FFPE-CUTAC和FACT-seq或标准CUT&Tag的轨迹。由于细胞类型的差异,作者将轨迹的比较限制在预计在所有细胞类型中表达相似的基因上。明显看出,H3K27ac CUTAC的配置文件比使用FACT-seq获得的配置文件要干净得多,对于冷冻小鼠肾脏的CUT&Tag控制数据也比敏感性高。为了对数据质量进行系统分析,作者使用MACS2进行了峰值调用,并比较了峰值调用的数量和FRiP值。为了确定FFPE-CUTAC配置文件捕获调节元素的程度,作者利用了ENCODE项目生成的候选cis-调节元素(cCRE)数据库,该数据库从所有进行概要分析的组织类型中调用了潜在的调节元素。作者得出结论, FFPE-CUTAC方案提供了高质量的数据,即使与标准的CUT&Tag进行比较也是如此。
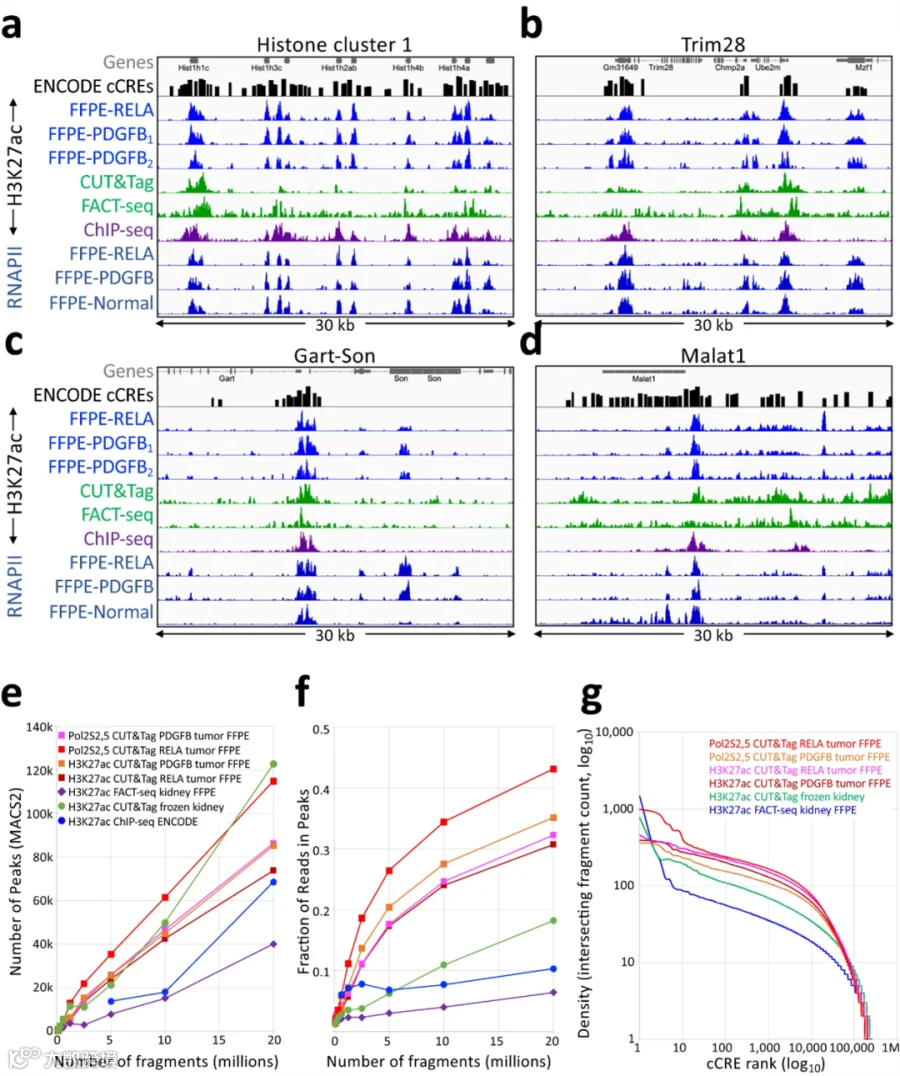
图3. H3K27ac FFPE-CUTAC与冷冻未固定样品的FACT-seq和CUT&Tag的比较
四、FFPE-CUTAC 图谱可区分脑肿瘤并揭示整体上调
几乎所有H3K27ac和RNAPII-Ser2,5p FFPE-CUTAC中看到的强峰都对应于cCRE数据库中的潜在调节元素,FFPE-CUTAC、FACT-seq和ChIP-seq之间的一致性。为了识别肿瘤特异性的候选调节元素,作者在三种不同的小鼠脑肿瘤(YAP1-, PDGFB- 和 RELA-驱动的肿瘤)与正常小鼠大脑之间进行了两两比较。结果表明,使用针对RNAPII或H3K27标记的抗体的FFPE-CUTAC能够通过几乎所有显著差异来区分肿瘤和正常大脑样本,这些差异代表了三种肿瘤相对于正常大脑的增加。
为了平衡每个基因型的样本贡献,作者合并了每种抗体(RNAPII-Ser5p、RNAPII-Ser2,5p或H3K27ac)或抗体组合(RNAPII-Ser5p + RNAPII-Ser2,5p)的多个FFPE-CUTAC实验的数据集。最后得出结论,根据活性RNAPII和H3K27ac标记的cCRE占用的差异,FFPE-CUTAC可以区分肿瘤之间和肿瘤与正常大脑之间的差异。
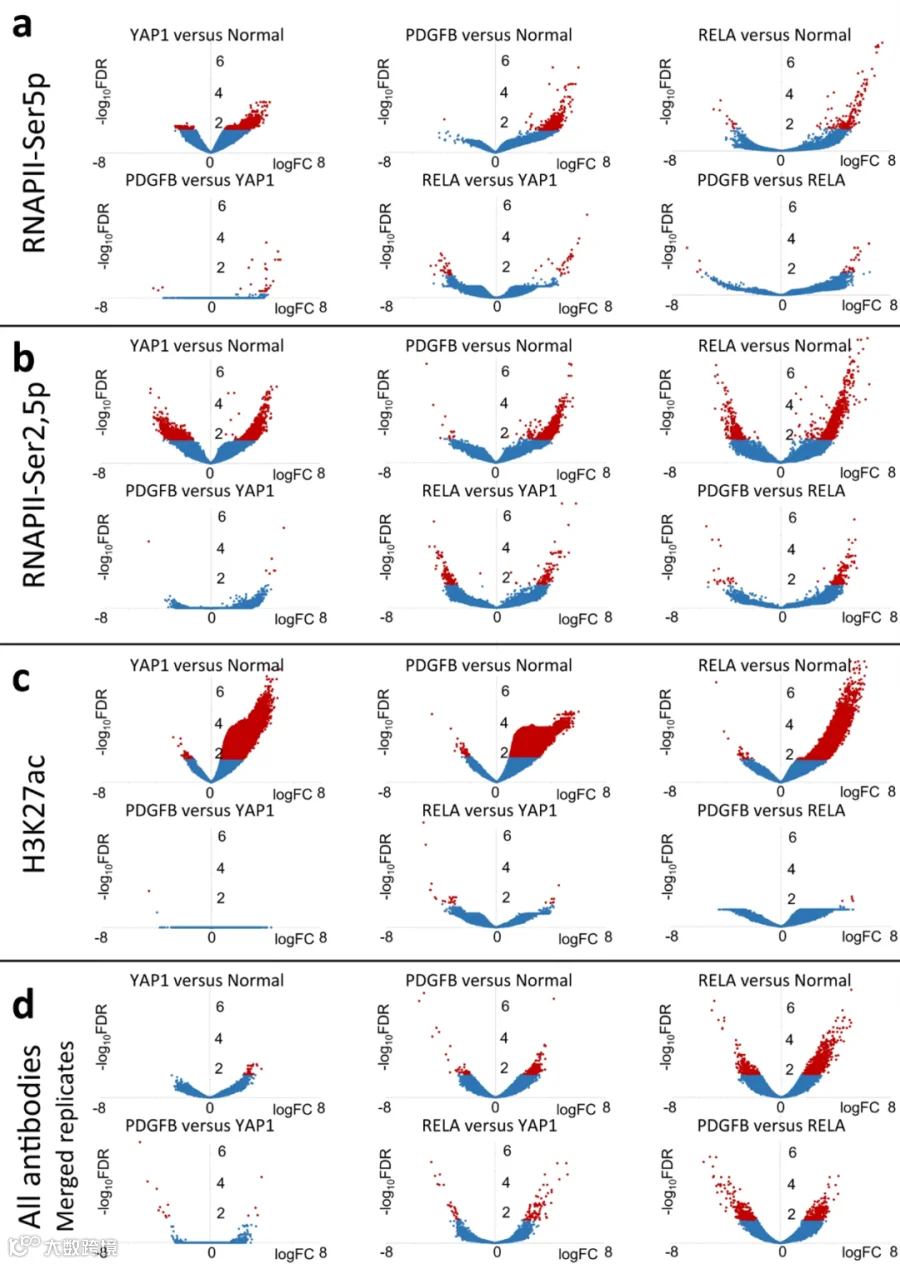
图4. FFPE-CUTAC样本之间成对比较的火山图
五、暂停态的RNAPII增加可精确定位调控元素的差异
为了鉴定区分肿瘤和正常状态以及肿瘤间的基因调控元素,作者采用了Voom/Limma分析。与肿瘤进展相关的报道中,最显著且高度表达的差异包括SET domain-containing 5(Setd5)启动子,Phosphoglucokinase(Pgk1)启动子,它们也来自PDGFB驱动的肿瘤和正常样本的比较,显示出肿瘤之间的明显差异。这些比较还突显了与肿瘤进展相关的其他基因,包括Connective tissue growth factor(Ccn2)启动子和Metallothionien 2 A(Mt2a)基因的内含子增强子。最后,虽然Testis Expressed 14(Tex14)基因尚未被报道与癌症有关,但这是前12个基因中唯一肿瘤/正常差异不明显的基因,与增加的暂停状态RNAPII在其他基因的增强子或启动子上与肿瘤进展相关的假设一致。
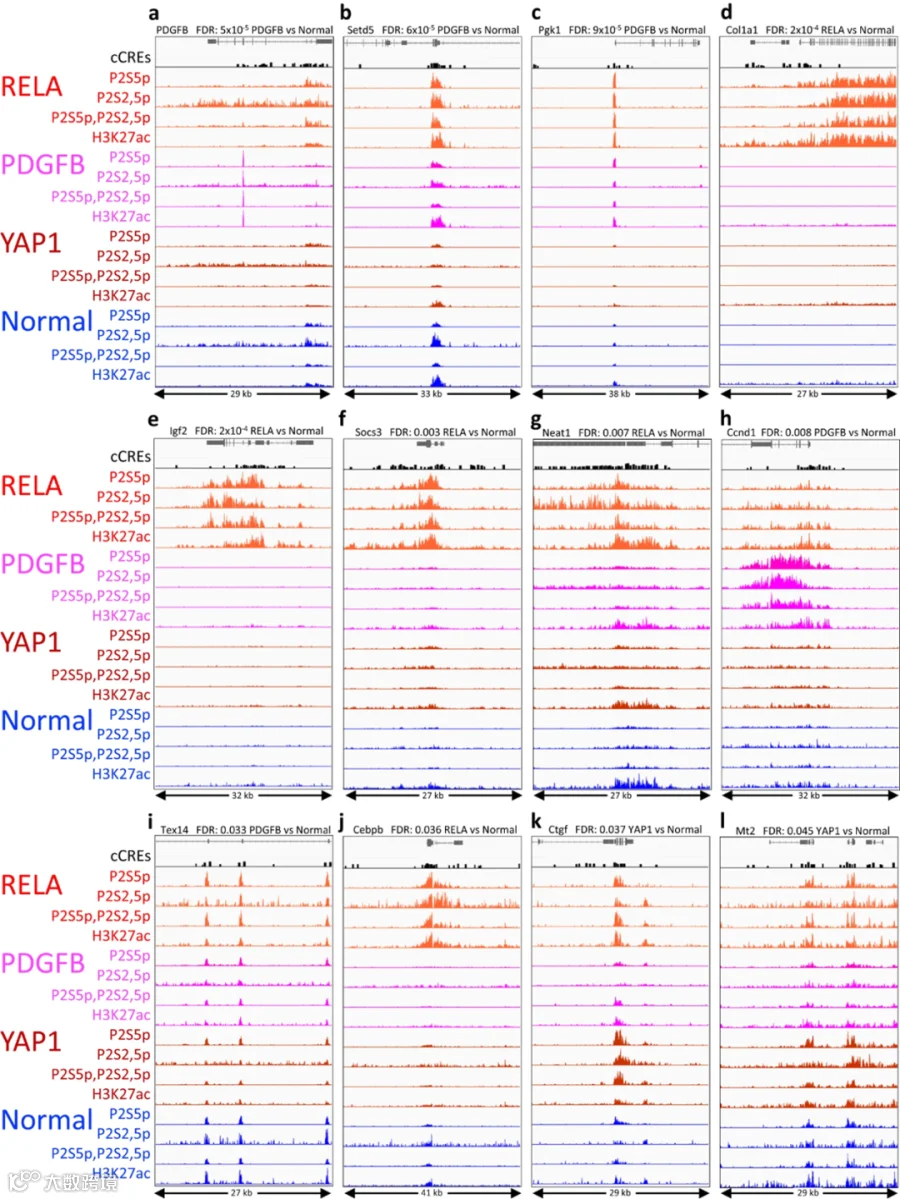
图5. 基于RNAPII-Ser5p FFPE-CUTAC比较,肿瘤与正常以及肿瘤之间最显著的差异
六、FFPE-CUTAC在同一FFPE内区分肿瘤和正常组织
作者在同一玻片上比较肿瘤和正常组织,使用了相对较大且在细胞学上有明显区别的ZFTA-RELA基因融合驱动的ependymomas,而PDGFB驱动的gliomas则更为分散。在测序后,作者进行了Voom/Limma分析,比较了在细胞学上主要为肿瘤的切片与主要为正常的切片。发现在两个复制的玻片中,最高下调的基因Mir124a-1hg是幽门螺杆菌感染的微RNA甲基化标记位点,与胃癌驱动基因甲基化相关。
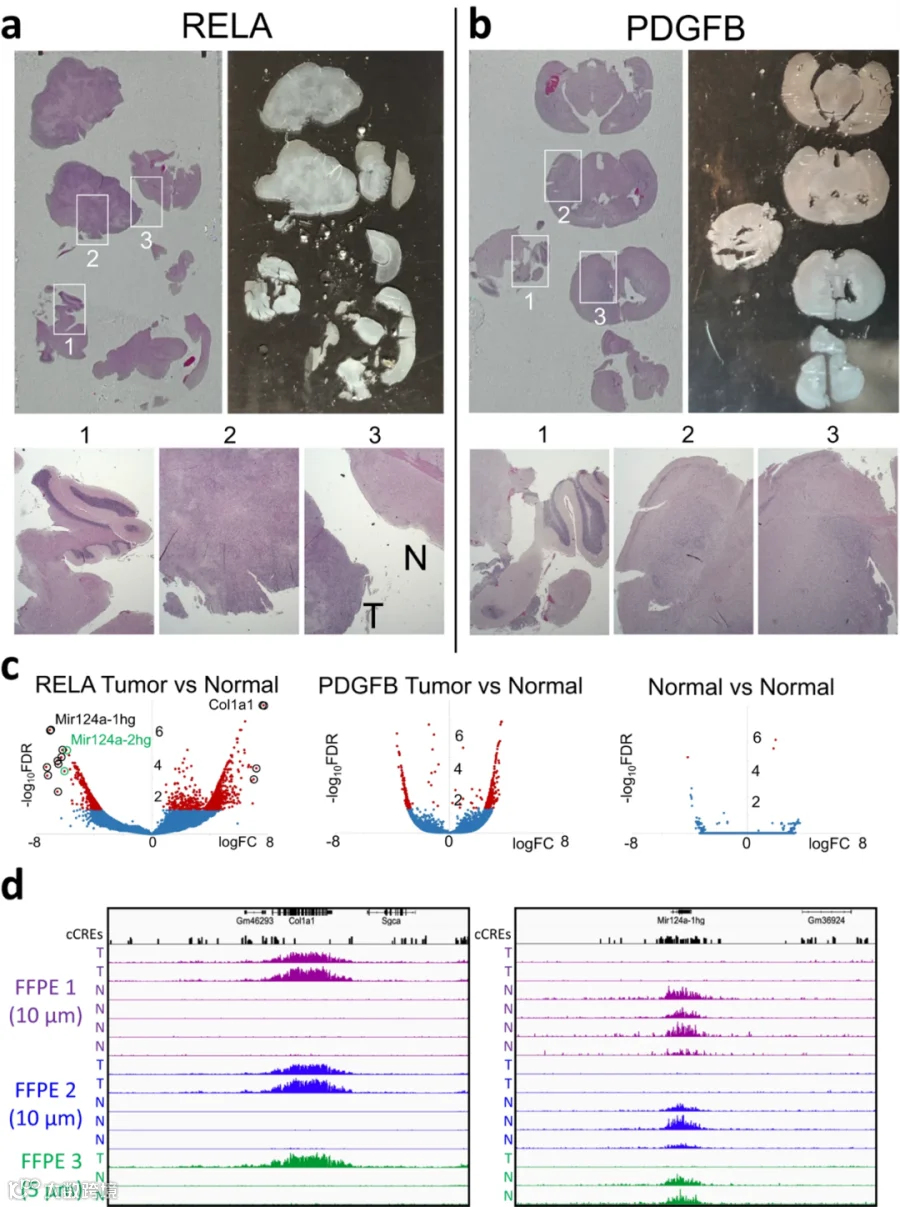
图6. FFPE-CUTAC在同一FFPE切片中区分肿瘤和正常组织
相比之下,这些基因在根据假发现率排名的RNA-seq列表中远远落后。与将大脑肿瘤和经过2天甲醛固定的正常组织相同,峰数和峰中读数的比例(FRiP)远高于FACT-seq FFPE肝脏,并且当下采样到相同数量的片段时,与cCRE的重叠度也更高。最后,火山图显示相对于正常肝脏,肝肿瘤的cCRE RNAPII占据在折叠变化和FDR方面都呈现净增加,类似于我们在比较大脑肿瘤与正常大脑时观察到的情况。作者得出结论,FFPE-CUTAC为不同组织类型的FFPE提供了高质量的数据。
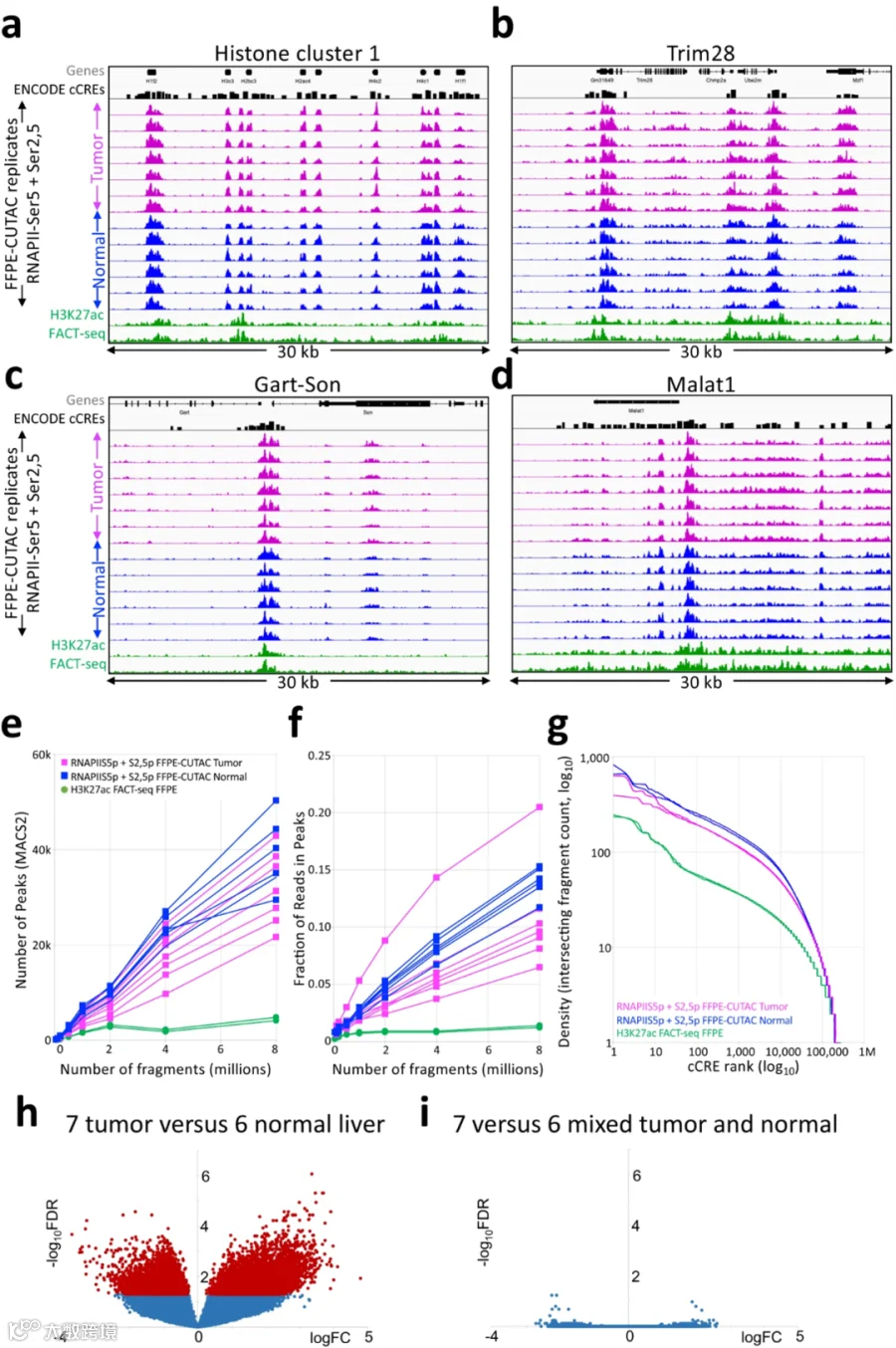
图7.FFPE-CUTAC从肝脏FFPEs生成高质量数据
七、FFPE-CUTAC与标准RNA-seq在转基因驱动的脑肿瘤方面的比较
为了对比FFPE-CUTAC的调控元素和RNA-seq的加工转录本,作者首先确定是否存在足够的重叠区域,将cCREs(候选启动子区域)与RNA-seq映射的已注释的5'-3'基因进行比较。发现FFPE-CUTAC和RNA-seq样本之间的比较则“模糊”,但仍然显示出很强的相关性。还确定了这两个数据集中相同基因在肿瘤和正常样本之间差异显著的程度。为了验证这些比较,作者在YAP1和YAP1的九个直接靶基因的FFPE-CUTAC和RNA-seq数据上进行了对比。正如预期的那样,FFPE-CUTAC数据主要富集在5'末端,而RNA-seq数据富集在3'末端。重要的是,都显示出了FFPE-CUTAC和CUTAC数据与先前发布的高质量RNA-seq数据在整体上具有极好的一致性。FFPE-CUTAC数据的高特异性、其识别和映射差异调控的微RNA的能力,以及其简单的实现和自动化潜力,使其成为发现功能性生物标志物的杰出模式。
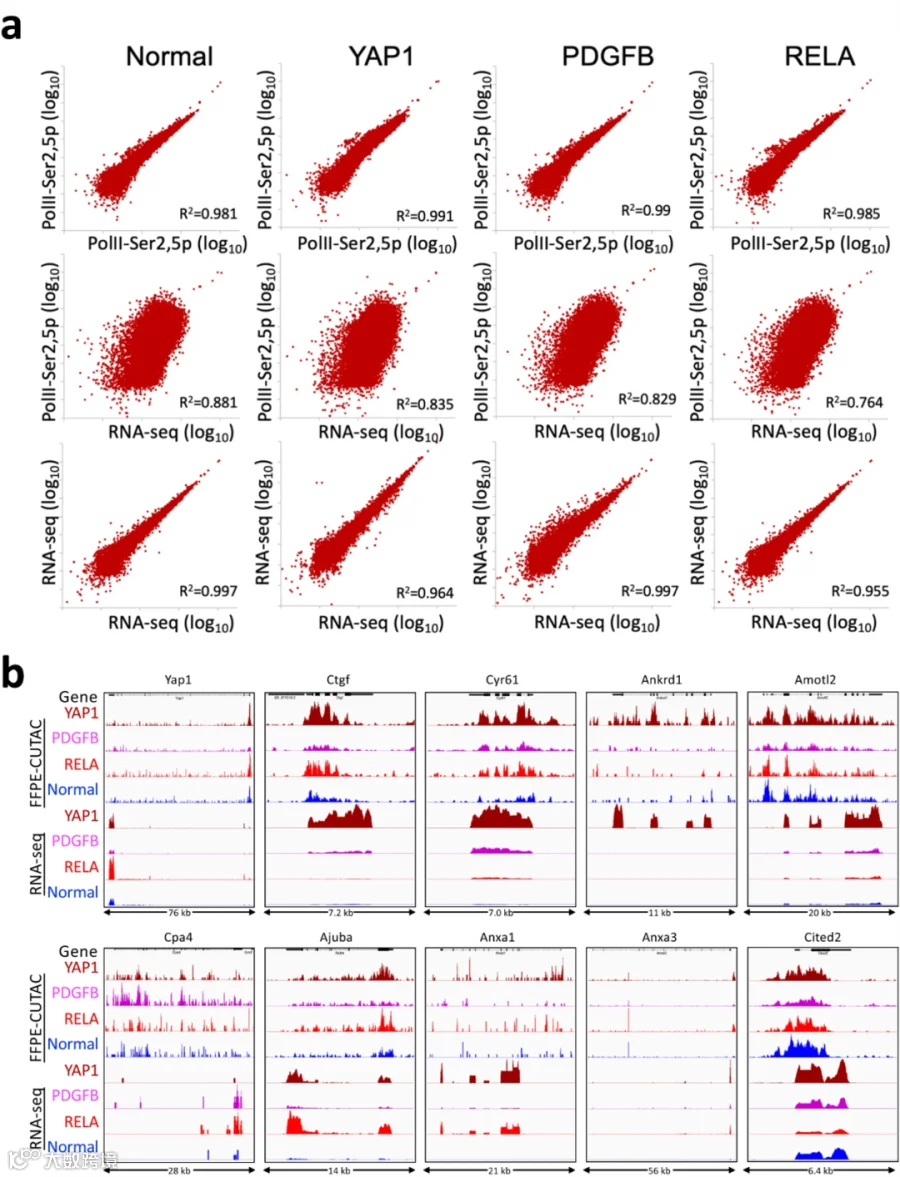
图8.FFPE-CUTAC和RNA-seq之间的比较

领克生物致力于新一代高通量测序技术(NGS)的应用和推广、生信分析、临床辅助诊断、产前检测、转化医学研究等领域。
业务包括单细胞多组学测序、基因组重测序、外显子测序、WGBS、RRBS、转录组测序、LncRNA测序、miRNA测序、ATAC-seq、CUT&Tag、Hi-C、4C-seq、m6A测序等前沿技术服务、各类组学数据的个性化分析服务以及临床疾病的辅助诊断、产前检测等。

欢迎咨询了解~
电话:0871-65399960
邮箱:service@biolinker.com


