中国科学院遗传与发育生物学研究所曹晓风院士团队在Advanced Science上发表了题为Genomic Variation Underpins Genetic Divergence and Differing Salt Resilience in Sesbaniabispinosa的研究论文。该研究构建了耐盐型和敏盐型刺田菁高质量参考基因组,解析了二倍体刺田菁自然群体演化规律,发现了二倍体田菁群体迁移到沿海地区,发生大尺度倒位变异导致群体分化,从而演化获得耐盐性状和主效基因。这项研究为豆科饲草和作物的抗逆分子育种提供了理论基础和基因资源。

该研究由未米生物提供
大豆
载体构建 基因编辑
遗传转化服务
研究背景
土壤盐碱化是全球农业生产面临的严峻挑战,据统计,全球超过 10% 的耕地受到盐胁迫影响,这不仅导致农作物产量下降,更对全球粮食安全构成重大威胁。盐生植物因具备在高盐环境中生长的独特适应性,成为挖掘耐盐基因资源、改良作物抗逆性的重要研究对象。然而,以往关于植物耐盐性的研究多集中于模式植物或低盐环境下的栽培作物,对盐生植物尤其是豆科盐生植物的基因组特征与耐盐机制探索较少。田菁属作为豆科重要类群,包含约 60 个热带亚热带物种,其中双刺田菁为二倍体植物,兼具耐盐性与经济价值,其叶片、种子可作为饲料,成熟种子还被部分印度部落食用,同时在土壤改良中发挥作用。双刺田菁的基因组信息、自然群体演化规律及耐盐分子机制均处于未知状态,极大限制了其基因资源的开发与利用,因此,解析双刺田菁的基因组特征与耐盐适应性机制具有重要的理论与应用价值。
关键发现
为填补这一研究空白,研究团队首先开展了双刺田菁自然群体的耐盐性筛选,从中国热带和亚热带地区收集了 51 个自然群体,其中 46 个群体可产生足量种子用于表型分析。通过建立标准化的苗期耐盐评价体系 —— 将幼苗培养至首片羽状复叶完全展开后用 300mM NaCl 处理,以存活率和细胞膜通透性作为评价指标,发现群体内耐盐性差异显著:15 个群体表现为耐盐表型,14 个为敏盐表型,其中耐盐品系 SbTA02的存活率高达 91.83±2.25%,敏盐品系 SbSA44 仅为 1.11±1.57%,且两者在植株形态、刺密度和生物量上也存在明显差异。台盼蓝染色实验进一步验证了耐盐性差异:盐胁迫前两品系根细胞均存活,而 300mM NaCl 处理 4h 后,SbSA44 根细胞死亡率显著上升并在 12h 达峰值,SbTA02 则维持低死亡率,证实了筛选出的两个品系可作为耐盐机制研究的理想材料。基于此,研究团队利用 PacBio HiFi 测序结合 Hi-C 技术,成功构建了 SbTA02 和 SbSA44 的高质量染色体水平基因组:SbTA02 基因组大小为 1090Mb,SbSA44 为 1094Mb,两者均包含 6 条染色体,分别由 10 个和 9 个 contig 组成,未组装缺口仅 4 个和 3 个,且均实现了 12 个染色体端粒中 9-10 个的完整组装;通过 CENH3 ChIP-seq 技术,还成功解析了 6 个大于 1Mb 的着丝粒区域,其特征为染色体中部的显著峰值。基因组完整性评估显示,两者 BUSCO 完整度均达 99.2%,单碱基准确率分别为 99.9997%(SbTA02)和 99.9993%(SbSA44),且转座元件占比约 73%,其中 LTR 逆转座子为主要类型并集中于基因组中央区域,这些高质量的基因组资源为后续研究奠定了坚实基础。

刺田菁群体耐盐筛选以及基因组组装
在基因组比较分析中,研究团队发现双刺田菁两个品系的基因组分化主要源于着丝粒及近着丝粒区域的结构变异,其中最显著的是两个大片段倒位:5 号染色体上 74.79-101.93Mb 区间的 > 27Mb 倒位,以及 6 号染色体上 53.86-102.58Mb 区间的≈49Mb 倒位,Hi-C 数据进一步证实了这些倒位的存在。结构变异分析显示,两品系间存在 954.4Mb 的共线性序列,而 12.8% 的差异序列中,约 104.2Mb 来自倒位,且 91% 的倒位区域与着丝粒或近着丝粒重叠,表明这些区域是基因组分化的 “热点”。系统发育分析基于单拷贝蛋白编码基因构建进化树,结果显示 SbTA02 与 SbSA44 约在 0.7 百万年前(Mya)分化,且两者与四棱田菁 A 亚基因组的最近共同祖先可追溯至 1.5Mya,与 B 亚基因组则为 7.8Mya,同义替换率分析进一步验证了这一演化时间线,揭示了双刺田菁在田菁属中的演化地位。
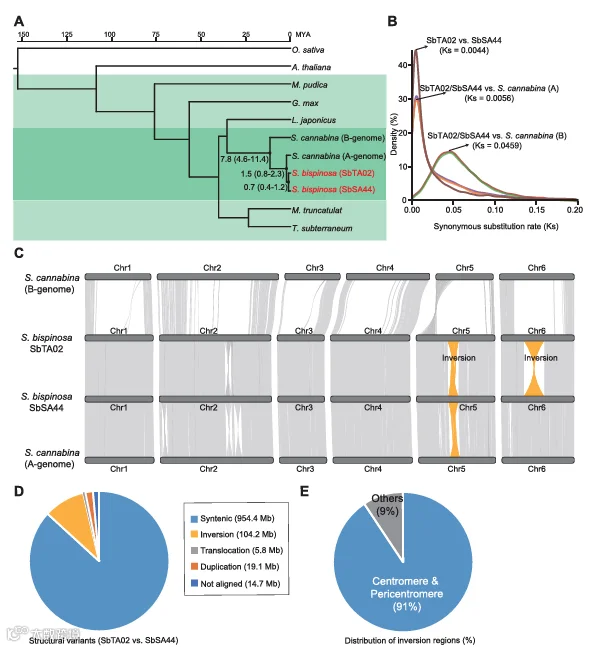
S. bispinosa两个基因组的进化和比较分析结果
为探究基因组变异对自然群体的影响,研究团队对 51 个双刺田菁群体进行全基因组重测序,获得约 1145Gb 数据,平均每个群体覆盖深度 20.6×,共鉴定出 2918655 个高质量 SNP,平均每千碱基 2.7 个 SNP。基于这些 SNP 的主成分分析(PCA)显示,所有群体可明确分为两个类群:内陆群体(AI)与沿海群体(AC),其中 AC 群体分布于沿海城市,AI 群体集中于内陆地区;进化树分析与群体结构分析进一步证实了这一群体分化模式。深入分析发现,5 号染色体的≈27Mb 倒位是驱动群体分化的关键因素:AC 群体的测序 reads 可匹配 SbTA02 基因组中的该倒位断点,而 AI 群体则无法匹配,这一倒位基因型分组与 PCA、进化树的分组结果完全一致;与之形成对比的是,6 号染色体的≈49Mb 倒位仅在 20 个 AC 群体中的 12 个中存在,表明其对群体分化的影响较小。群体遗传参数分析显示,AI 与 AC 群体的成对固定指数(FST)达 0.3876,提示显著的遗传分化,且 AC 群体的核苷酸多样性显著低于 AI 群体,结合地理分布推测,双刺田菁可能起源于西南内陆地区,并逐渐向东部沿海扩散,沿海高盐环境驱动了群体的适应性分化。此外,5 号染色体 34.0-136.7Mb 区间形成了显著的遗传分化区域,该区域的 FST 值处于全基因组前 5%,进一步证实了这一区间在群体分化中的核心作用。
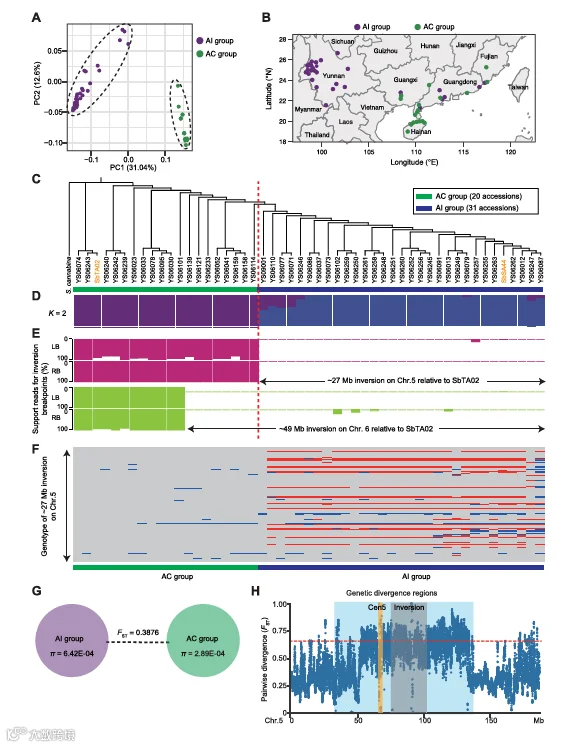
S. bispinosa种群的基因组分析结果
揭示了高度分化的遗传区域
为解析双刺田菁耐盐性的分子基础,研究团队开展了基于存活率的全基因组关联分析,在 5 号染色体的 GDRs 区域检测到 6 个显著的耐盐关联信号,这些信号集中于 42.71-42.90Mb 区间,对应三个候选基因:花青素合成酶基因 SbANS、PGR5 样蛋白 1A 基因和细胞色素 P450 基因 CYP87A2。进一步的 RNA-seq 分析显示,在 300mM NaCl 处理的不同时间点,仅SbANS在耐盐品系 SbTA02 中的表达量显著高于敏盐品系 SbSA44,另两个基因则无显著差异且表达量较低。单倍型分析基于 SbANS 附近的 4 个显著 SNP 将群体分为两种单倍型:Hap.A 与 Hap.B,其中携带 Hap.A 的群体存活率显著高于 Hap.B,且 55% 的 AC 群体携带耐盐 Hap.A,100% 的 AI 群体携带敏盐 Hap.B,表明 SbANS 的变异与群体耐盐性分化紧密相关。qRT-PCR 与花青素含量测定进一步验证:耐盐群体在无盐胁迫时 SbANS 表达量已显著高于敏盐群体,且其根部花青素含量也更高,而花青素可通过清除活性氧、缓解离子与渗透损伤增强耐盐性;异源功能验证显示,将 SbTA02 的 SbANS 基因导入大豆后,转基因大豆的耐盐性显著提升,证实了该基因耐盐功能的保守性。
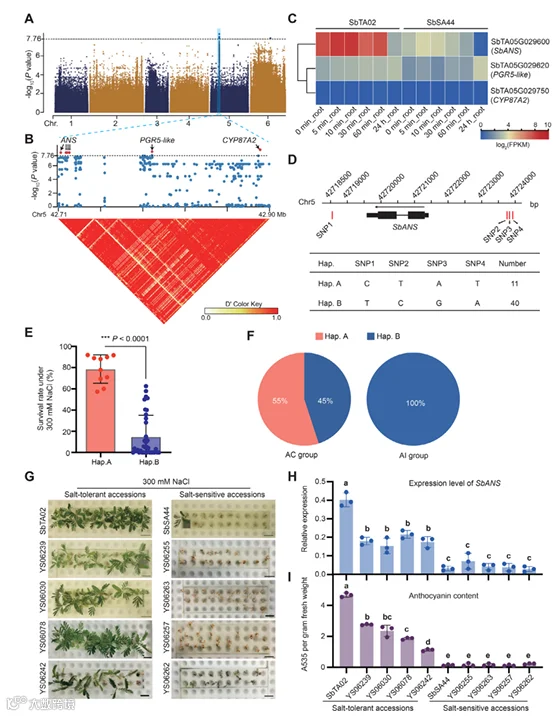
S. bispinosa耐盐性与花青素合成酶基因SbANS的关联分析结果
该研究首次构建了双刺田菁耐盐与敏盐品系的高质量参考基因组,通过多组学分析系统揭示了双刺田菁耐盐适应性的遗传基础:着丝粒与近着丝粒区域的大尺度倒位驱动了自然群体的地理分化,形成了适应不同盐环境的内陆与沿海类群;而花青素合成酶基因 SbANS 的自然变异则是调控耐盐性的关键,其组成型高表达与花青素积累构成了双刺田菁适应高盐环境的核心分子机制。这些发现不仅为田菁属的基因组演化研究提供了新视角,更鉴定出具有应用价值的耐盐基因 SbANS,为豆科饲草与作物的耐盐分子育种提供了重要的理论依据与基因资源,对推动盐碱地农业的可持续发展具有重要意义。



